 Responsable
Responsable
 Adresse
Adresse Laboratoire Physiologie Cellulaire & Végétale
CEA-Grenoble
17 avenue des Martyrs
38 054 Grenoble cedex 9
France
 Membres de l'équipe
KUNTZ Marcel
Membres de l'équipe
KUNTZ Marcel, Directeur de recherche CNRS,
Marcel.Kuntz[@]cea.fr
MOYET Lucas, Assistant Ingénieur INRAE,
Lucas.Moyet[@]cea.fr
PULLARA Sara, Étudiante en thèse,
Sara.Pullara[@]cea.fr
ROLLAND Norbert, Directeur de recherche CNRS,
Norbert.Rolland[@]cea.fr
WAHIDI Mohamad, Étudiant en thèse,
Mohamad.Wahidi[@]cea.fr
YUAN Yizhong, Étudiant en thèse,
Yizhong.Yuan[@]cea.fr
 Anciens membres de l'équipe
Anciens membres de l'équipe Introduction
Introduction
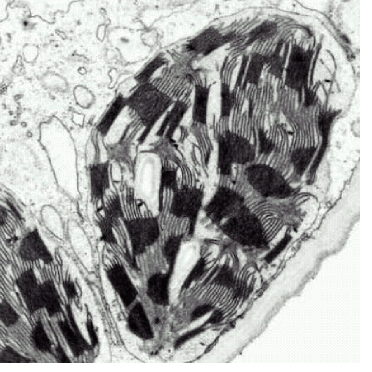 Le chloroplaste est le centre de production d'un nombre important de biomolécules (acides gras, acides aminés, sucres, vitamines, terpènes, alcaloïdes, phénols etc) qui présentent un grand intérêt pour les bioénergies comme pour l'alimentation et la santé humaine. Véritable usine énergétique de la cellule végétale, cet organite photosynthétique est responsable de la synthèse de la totalité de la biomasse de la plante, et constitue la principale « pompe à CO2 », agissant ainsi sur l'environnement et le climat.
Le chloroplaste est le centre de production d'un nombre important de biomolécules (acides gras, acides aminés, sucres, vitamines, terpènes, alcaloïdes, phénols etc) qui présentent un grand intérêt pour les bioénergies comme pour l'alimentation et la santé humaine. Véritable usine énergétique de la cellule végétale, cet organite photosynthétique est responsable de la synthèse de la totalité de la biomasse de la plante, et constitue la principale « pompe à CO2 », agissant ainsi sur l'environnement et le climat. |
 Activités de recherche
Activités de recherche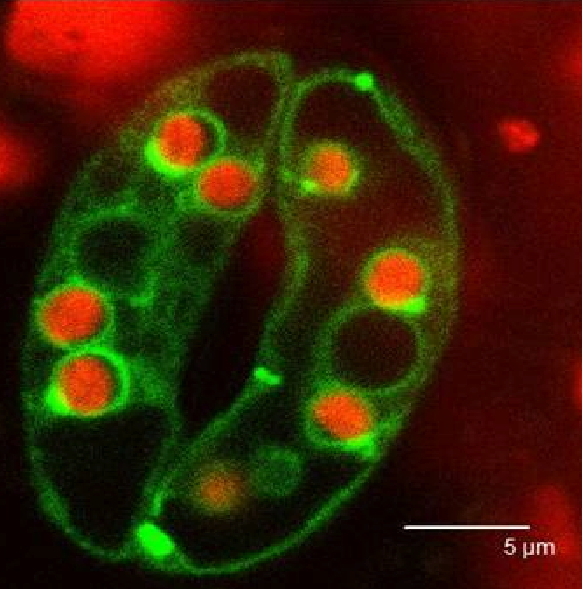
Un des aspects le plus fascinant (et le moins étudié) des organismes photosynthétiques est leur capacité à gérer des variations rapides des conditions environnementales et à réorienter leur métabolisme en réponse à ce que l'on dénomme habituellement « stress » (lumière, nutriments, froid, etc…). De la rapidité de ces réponses et de leur efficacité dépend le sort de la plante dans les différentes conditions qu'elle rencontrera au cours de son cycle de vie. Ce type de réponses implique à court terme des changements métaboliques, à plus long terme des changements d'expression génique et donc de composition protéique. Notre approche vise à déchiffrer les réseaux de régulations qui contrôlent la dynamique du protéome du chloroplaste afin de mieux comprendre la capacité des plantes à répondre aux conditions variables de l'environnement.
Les approches utilisées dans l'équipe sont la protéomique à grande échelle, la microscopie confocale, des mesures de la synthèse de pigments et de vitamines, la caractérisation de transports d'ions ou de protéines. Une approche de modélisation analytique est aussi utilisée pour intégrer des données de biologie cellulaire et de biochimie. Nos organismes modèles sont les plantes supérieures (Arabidopsis, tomate, épinard…).
 Activités de recherche :
Quelques faits-marquants
Activités de recherche :
Quelques faits-marquants Publications de l'équipe
Publications de l'équipe
 Sélection de publications
Sélection de publications
Moyet L, Salvi D, Bouchnak I, Miras S, Perrot L, Kuntz M and Rolland N Calmodulin is involved in the dual subcellular location of two chloroplast proteins.
Journal of Biological Chemistry, 2019,
294(46): 17543-17554
Bouchnak I, Brugière S, Moyet L, Le Gall S, Salvi D, Kuntz M, Tardif M and Rolland N
Unravelling hidden components of the chloroplast envelope proteome: Opportunities and limits of better MS sensitivity.
Molecular & Cellular Proteomics, 2019,
18(7): 1285–1306
Gloaguen P, Bournais S, Alban C, Ravanel S, Seigneurin-Berny D, Matringe M, Tardif M, Kuntz M, Ferro M, Bruley C, Rolland N, Vandenbrouck Y and Curien G ChloroKB: A Web application for the integration of knowledge related to chloroplast metabolic network.
Plant Physiology, 2017,
174(2): 922-934
Sautron E, Giustini C, Dang T, Moyet L, Salvi D, Crouzy S, Rolland N, Catty P and Seigneurin-Berny D Identification of two conserved residues involved in copper release from chloroplast P
IB-1-ATPases.
Journal of Biological Chemistry, 2016,
291(38): 20136–20148
Tomizioli M, Lazar C, Brugiere S, Burger T, Salvi D, Gatto L, Moyet L, Breckels LM, Hesse AM, Lilley KS, Seigneurin-Berny D, Finazzi G, Rolland N and Ferro M Deciphering thylakoid sub-compartments using a mass spectrometry-based approach.
Molecular and Cellular Proteomics, 2014,
13(8): 2147-2167
Rolland N, Curien G, Finazzi G, Kuntz M, Maréchal E, Matringe M, Ravanel S and Seigneurin-Berny D The biosynthetic capacities of the plastids and integration between cytoplasmic and chloroplast processes.
Annual Review of Genetics, 2012,
46: 233-264
Tardif M, Atteia A, Specht M, Cogne G, Rolland N, Brugiere S, Hippler M, Ferro M, Bruley C, Peltier G, Vallon O and Cournac L PredAlgo, a new subcellular localization prediction tool dedicated to green algae.
Molecular Biology and Evolution, 2012,
29(12): 3625-3639
Catty P, Boutigny S, Miras R, Joyard J, Rolland N and Seigneurin-Berny D Biochemical characterization of AtHMA6/PAA1, a chloroplast envelope Cu(I)-ATPase.
Journal of Biological Chemistry, 2011,
286(42): 36188–36197
Ferro M, Brugiere S, Salvi D, Seigneurin-Berny D, Court M, Moyet L, Ramus C, Miras S, Mellal M, Le Gall S, Kieffer-Jaquinod S, Bruley C, Garin J, Joyard J, Masselon C and Rolland N AT_CHLORO: A comprehensive chloroplast proteome database with subplastidiallocalization and curated information on envelope proteins.
Molecular and Cellular Proteomics, 2010,
9(1): 1063-1084
Joyard J, Ferro M, Masselon C, Seigneurin-Berny D, Salvi D, Garin J and Rolland N Chloroplast proteomics highlights the subcellular compartmentation of lipid metabolism.
Progress in Lipid Research, 2010, 49(2): 128-158
Atteia A, Adrait A, Brugiere S, Tardif M, van Lis R, Deusch O, Dagan T, Kuhn L, Gontero B, Martin W, Garin J, Joyard J and Rolland N
A proteomic survey of
Chlamydomonas reinhardtii mitochondria sheds new light on the metabolic plasticity of the organelle and on the nature of the α-proteobacterial mitochondrial ancestor.
Molecular Biology and Evolution, 2009,
26(7): 1533-1548
Miras S, Salvi D, Piette L, Seigneurin-Berny D, Grunwald D, Reinbothe C, Joyard J, Reinbothe S and Rolland N TOC159- and TOC75-independent import of a transit sequence-less precursor into the inner envelope of chloroplasts.
Journal of Biological Chemistry, 2007,
282(40): 29482-29492
Seigneurin-Berny D, Gravot A, Auroy P, Mazard C, Kraut A, Finazzi G, Grunwald D, Rappaport F, Vavasseur A, Joyard J, Richaud P and Rolland N
HMA1, a new Cu-ATPase of the chloroplast envelope, is essential for growth under adverse light conditions.
Journal of Biological Chemistry, 2006,
281(5): 2882-2892
Villarejo A, Burén S, Larsson S, Déjardin A, Monné M, Rudhe C, Karlsson J, Jansson S, Lerouge P, Rolland N, von Heijne G, Grebe M, Bako L and Samuelsson G Evidence for a protein transported through the secretory pathway en route to the higher plant chloroplast.
Nature Cell Biology, 2005,
7(12): 1224-1231 | |
 |
Ferro M, Salvi D, Brugiere S, Miras S, Kowalski S, Louwagie M, Garin J, Joyard J and Rolland N
Proteomics of the chloroplast envelope membranes from
Arabidopsis thaliana.
Molecular and Cellular Proteomics, 2003,
2(5): 325-345
Ferro M, Salvi D, Rivière-Rolland H, Vermat T, Seigneurin-Berny D, Grunwald D, Garin J, Joyard J and Rolland N
Integral membrane proteins of the chloroplast envelope: Identification and subcellular localization of new transporters.
Proceedings of the National Academy of Sciences USA, 2002,
99: 11487-11492 | |
 |
Miras S, Salvi D, Ferro M, Grunwald D, Garin J, Joyard J and Rolland N
Non canonical transit peptide for import into the chloroplast.
Journal of Biological Chemistry, 2002,
277: 47770-47778
 Mots clés
Mots clés Chloroplaste, Métabolisme, Enveloppe du chloroplaste, Transports, ATPases, Cuivre, Biogenèse du chloroplaste, Plante, Physiologie, Biochimie, Protéomique, Biologie des systèmes.
 Projets collaboratifs en cours
Projets collaboratifs en cours • Grant ANR CE12 2018. Projet "
Polyglot". Coordinateur de l’équipe Norbert Rolland. 2018-2023.
• Grant H2020-SFS-2018-1. Projet "
CSA CropBooster-P". Participant au projet Norbert Rolland. 2018-2022.
 Projets achevés
Projets achevés • Grant INRA & Labex GRAL. Projet "
Chloroplast biogenesis". Coordinateur du projet Norbert Rolland. 2015-2018.
• Grant INRA. Projet "
HMA1". Coordinateurs du projet Daphné Berny/Norbert Rolland. 2014-2015.
• Grant PhD Labex GRAL & CEA. Projet "
ATPases". Coordinateur du projet Daphné Berny. 2012-2015.
• Grant Engineer Labex GRAL. Projet "
Chloroplast". Coordinateur du projet Norbert Rolland. 2012-2015.
• Grant ANR Genomics and Plant Biotechnologies. Projet "Chloro-Types". Coordinateur du projet Norbert Rolland. 2011-2014.
• Grant ANR Blanc 2010. Projet "Chloro-Pro". Coordinateur Norbert Rolland. 2011-2014.
• Grant PhD CEA IRTELIS. Coordinateur du projet Gilles Curien/Norbert Rolland. 2010-2013.
• Grant INRA. Project "Fib". Coordinateurs du projet Michel Matringe/Marcel Kuntz. 2011.
• Grant ANR Génoplante. Projet "Glyco-Chloroplast". Coordinateur de l'équipe Norbert Rolland. 2007-2010.
• Grant CNRS Post-doc. Projet “Membrane proteins”. Coordinateur du projet Norbert Rolland. 2008-2009.
• Grant CEA. Projet "CEA-PM: Screening of Alternative Expression systems for the Production of Membrane Proteins". Coordinateur du projet Norbert Rolland. 2007-2009.
• Grant PhD CEA. Projet “Atpases”. Coordinateurs du projet Daphné Berny/Norbert Rolland. 2006-2009.
• Grant CNRS Post-doc. Projet “Chlamydomonas proteomics”. Coordinateur du projet Norbert Rolland. 2005-2006.
• Grant Région Rhône-Alpes/CEA. Projet "Development of an
in vitro expression technology for the production of membrane proteins". Coordinateur du projet Norbert Rolland. 2003-2005.
• Grant Génoplante 2 - New Tools (phase 2). Projet "Characterization of
Arabidopsis thaliana gene products: Hydrophobic proteome of membranes". Coordinateur du projet Norbert Rolland. 2002 -2005.
• Grant PhD CEA. Projet “Alternative chloroplast targeting pathways”. Coordinateur du projet Norbert Rolland. 2001-2004.
• Grant Génoplante 2 - New tools. Projet "Chloroplast microarrays". Coordinateur du projet Norbert Rolland. 2001-2003.
• Grant CEA National Program of Nuclear Toxicology. Projet "Impact of radionuclides on the metabolism of higher plants". Coordinateur du projet Norbert Rolland. 2001-2003.
• Grant Génoplante I - Functional Analyses (AF 1999-035). Projet "Functional genomics of membrane transport systems in
Arabidopsis thaliana". Coordinateur de l'équipe Norbert Rolland. 2000-2001.
• Grant Génoplante I - New tools (NO 1999-3663). Projet "Characterization of
Arabidopsis thaliana gene products: Structural and functional analysis of cell and subcellular proteomes". Coordinateur de l'équipe Norbert Rolland. 2000-2001.
• Grant CEA "Action Incitative Chimie". Projet "Physiology and genetics of transport of radionuclides in plants". Coordinateur de l'équipe Norbert Rolland. 1999-2001.
• Grant CNRS “Physique et Chimie du Vivant”. Projet 1998-122 "Subcellular plant proteome: Subcellular localization of gene products of
Arabidopsis thaliana". Coordinateur du projet Norbert Rolland. 1998-2000.