Les microalgues sont des micro-organismes unicellulaires photosynthétiques qui ont la capacité de stocker de l'énergie sous forme de lipides en quantité très importante. L'exploitation de cette production lipidique représente un intérêt croissant pour de nombreuses applications biotechnologiques, comme la production de bio-carburants. Dans le cadre de cette étude, les chercheurs du LPCV ont pris pour modèle la microalgue oléagineuse
Microchloropsis gaditana pour sa capacité à produire à des taux élevés de la
biomasse* et des lipides, et pour sa tolérance à des conditions de culture variées (pH, température, salinité). Au-delà d'avoir un métabolisme complexe, de par la particularité de son histoire évolutive,
Microchloropsis gaditana produit et accumule des lipides sous carence du milieu en azote, stoppant alors sa fabrication de biomasse. Afin d'optimiser et d'améliorer le rendement de cette microalgue, une approche
in silico a été développée : iMgadit23, un
modèle métabolique à l'échelle du génome (GEM)* pour
Microchloropsis gaditana.
Au-delà de prédire les
flux métaboliques*, qui se basent sur les contraintes du système, les GEMs permettent de prédire l'influence de facteurs génétiques et environnementaux sur les
phénotypes cellulaires*.
iMgadit23 est un nouveau modèle métabolique de
Microchloropsis gaditana avec un métabolisme lipidique complet et validé. Les voies métaboliques ont toutes été exhaustivement annotées et sont visualisables à partir d'une carte 2D ESCHER (https://escher.github.io).
Après validation du modèle, à travers des caractéristiques intrinsèques de qualité comme l'équilibre des réactions, les annotations, …, mais également à partir de données expérimentales, ce modèle a permis de simuler le comportement de la souche dans différents milieux et conditions génétiques et a permis d'élucider le phénotype métabolique d'une souche mutante présentant un profil lipidique très intéressant (multiplication de la quantité de lipides par un facteur 8 par rapport à la souche sauvage).
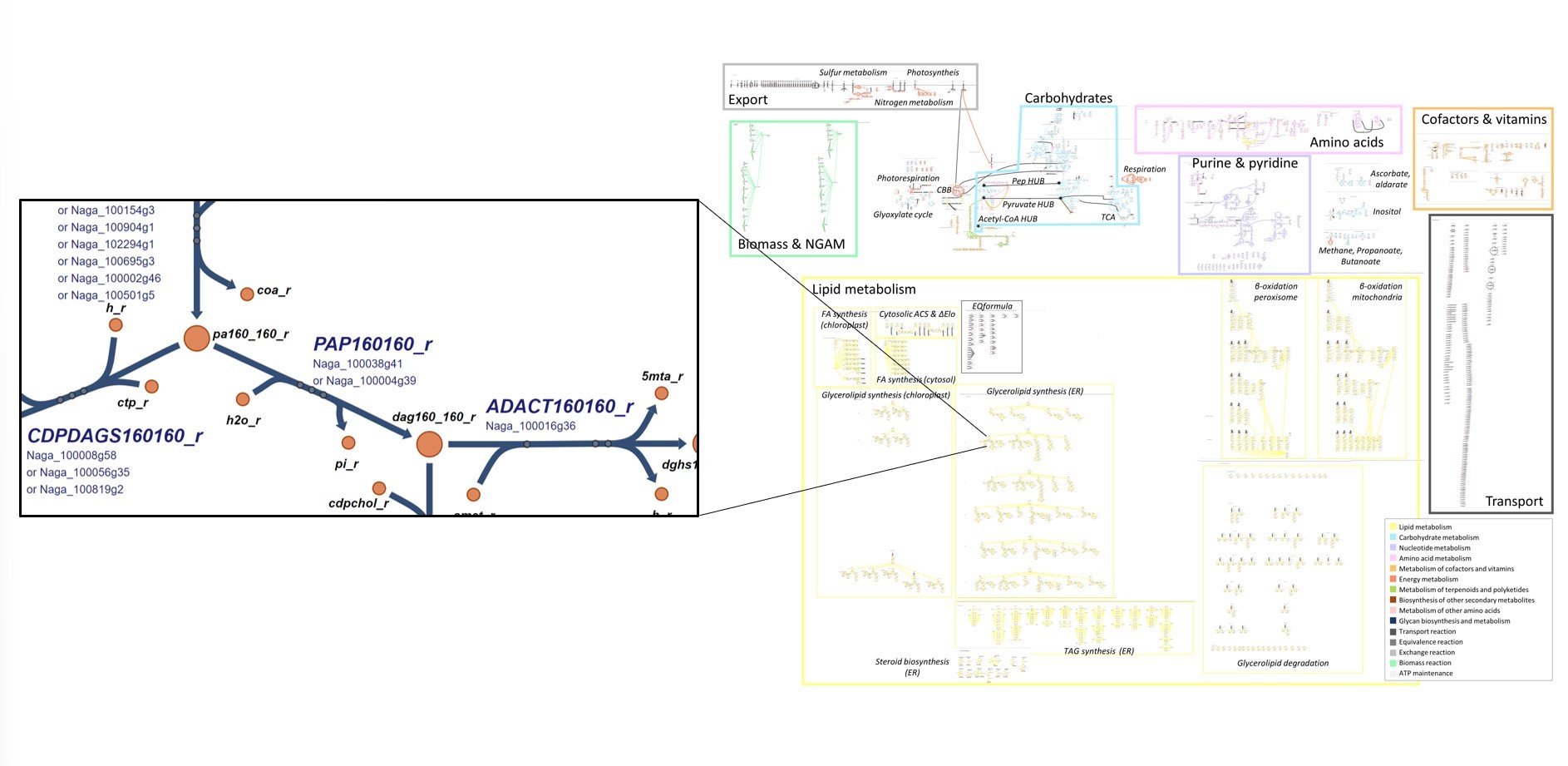
© CEA-Irig/LPCV/Lipid/J. Jouhet
Figure: Carte Escher -Visualisation du modèle métabolique de Microchloropsis gaditana.
Le développement de ce nouveau modèle métabolique à l'échelle du génome, iMgadit23, permet de modéliser intégralement, pour la première fois, le métabolisme lipidique de
Microchloropsis gaditana rendant ainsi possible, pour un moindre coût, l'élucidation de phénotype métabolique de souche mutante candidate ayant un profil lipidique présentant un meilleur rendement que la souche sauvage.
Le métabolisme lipidique ayant été entièrement détaillé, la stratégie utilisée pour construire ce modèle est destinée à pouvoir être appliquée et transférée à tout autre organisme vivant.
Métabolisme des lipides*: Ensemble des réactions chimiques permettant la fabrication, la transformation et le stockage des lipides au sein d'un organisme.
Biomasse* : Matière organique produite incluant l'ensemble des molécules organiques (lipides, protéines, glucides) constituant la matière vivante.
Modèle métabolique à l'échelle du génome (GEM)* : Réseau métabolique rassemblant l'ensemble des informations métaboliques connues d'un système biologique : les métabolites, les réactions, les gènes, les enzymes et les règles « gène-protéine-réaction » associées.
Flux métaboliques* : vitesse de synthèse des produits.
Phénotype cellulaire* : Ensemble des caractéristiques observables d'une cellule résultant de l'expression de ses gènes et de l'influence de son environnement.
Tutelles UMR : CEA, CNRS, INRAE, UGA
Financements : Cifre PhD (TotalEnergies&CEA) [2020/1063] et GRAL, [ANR-17-EURE-0003]
Collaborations : LPCV, TotalEnergies (France), SilicoLife Lda (Portugal).